Loading AI tools
chemische Verbindung Aus Wikipedia, der freien Enzyklopädie
Selenocystein ist eine Aminosäure. L-Selenocystein (Abk. Sec oder U) ist die 21. proteinogene L-Aminosäure und ein reaktives Analogon des natürlichen L-Cysteins. Selenocystein enthält statt des Schwefelatoms ein Selenatom.
| Strukturformel | ||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
 | ||||||||||||||||||||||
| Struktur des natürlich vorkommenden L-Selenocysteins | ||||||||||||||||||||||
| Allgemeines | ||||||||||||||||||||||
| Name | Selenocystein | |||||||||||||||||||||
| Andere Namen |
| |||||||||||||||||||||
| Summenformel | C3H7NO2Se | |||||||||||||||||||||
| Externe Identifikatoren/Datenbanken | ||||||||||||||||||||||
| ||||||||||||||||||||||
| Eigenschaften | ||||||||||||||||||||||
| Molare Masse | 168,0 g·mol−1 | |||||||||||||||||||||
| Sicherheitshinweise | ||||||||||||||||||||||
| ||||||||||||||||||||||
| Soweit möglich und gebräuchlich, werden SI-Einheiten verwendet. Wenn nicht anders vermerkt, gelten die angegebenen Daten bei Standardbedingungen (0 °C, 1000 hPa). | ||||||||||||||||||||||
Selenocystein kann in den enantiomeren Formen D und L vorliegen, wobei in Proteinen nur die L-Form, synonym auch (R)-Selenocystein, vorkommt. D-Selenocystein ist enantiomer zu L-Selenocystein und besitzt nur geringe Bedeutung; in der wissenschaftlichen Literatur steht „Selenocystein“ (ohne Präfix) stets für L-Selenocystein.
| Isomere von Selenocystein | ||
| Name | L-Selenocystein | D-Selenocystein |
| Andere Namen | (R)-Selenocystein | (S)-Selenocystein |
| Strukturformel | 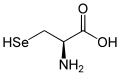 |  |
| CAS-Nummer | 10236-58-5 | 176300-66-6 |
| 3614-08-2 (DL) | ||
| EG-Nummer | 808-428-7 | – |
| – (DL) | ||
| ECHA-Infocard | 100.236.386 | – |
| – (DL) | ||
| PubChem | 25076 | 5460539 |
| 6326972 (DL) | ||
| Wikidata | Q408663 | Q27110363 |
| Q28529717 (DL) | ||
L-Selenocystein ist mit der Aminosäure L-Cystein chemisch nahe verwandt, besitzt jedoch eine niedrigere Säurekonstante von pKs = 5,3 für die Selenolgruppe im Vergleich zu pKs = 8–10 für die Thiolgruppe des L-Cysteins. Auch ist Selenocystein redoxaktiver als Cystein. Diese Eigenschaften dürften ein wesentlicher Grund für den Einbau von L-Selenocystein in Enzyme sein.

Selenocystein liegt überwiegend als inneres Salz bzw. Zwitterion vor, dessen Bildung dadurch zu erklären ist, dass das Proton von der Carboxygruppe abgespalten wird und vom freien Elektronenpaar des Stickstoffatoms der Aminogruppe aufgenommen wird.
Im elektrischen Feld wandert das Zwitterion nicht, da es als Ganzes ungeladen ist. Genaugenommen ist dies am isoelektrischen Punkt (bei einem bestimmten pH-Wert) der Fall, bei dem das Selenocystein auch seine geringste Löslichkeit in Wasser besitzt.
Der genetische Code gilt für alle Formen des Lebens, jedoch gibt es Besonderheiten. Während der Standardcode es Zellen ermöglicht, Proteine aus den 20 kanonischen α-Aminosäuren herzustellen, können sowohl Vertreter der Archaeen, Bakterien wie Eukaryoten während der Translation Selenocystein über einen als Recodierung bezeichneten Mechanismus einbauen. Der Einbau von L-Selenocystein als zusätzlicher proteinogener Aminosäure ermöglicht oft erst die Funktionsfähigkeit einiger essentieller Enzyme.
Da Menschen, vielen Tieren, einigen Algen und Einzellern das Codon für die lebensnotwendige 21. Aminosäure Selenocystein fehlt, wird das Stoppcodon UGA aufwändig über ein Umkodieren als Sec ausgelesen. Selbst in Insekten oder Nematoden bilden einige Vertreter Selenocystein, andere nicht. Pilze galten lange als Organismen, denen Selenocystein völlig fehlt, bis man auch hier unter rund tausend Arten neun Arten fand, die Selenocystein bilden.[2]
Man kennt über 30 eukaryotische und mehr als 15 bakterielle Selenocystein-haltige Proteine. So fand man bei Säugern u. a. verschiedene Glutathion-Peroxidasen, Tetraiodthyronin-Deiodasen oder große Thioredoxin-Reduktasen und bei Bakterien und Archaeen Formiat-Dehydrogenasen, Hydrogenasen, Protein-Komponenten der Glycin-Reduktase- und D-Prolin-Reduktase-Systeme und mehrere Enzyme des Stoffwechselwegs der Methanbildung als selenocysteinhaltige Enzyme.
Viele der Enzyme vermitteln Redox-Reaktionen. Bei ihnen befindet sich das reaktive Selenocystein im aktiven Zentrum. Bedeutung für Eukaryonten hat die Glutathion-Peroxidase als Teil der zellulären Abwehr von Schäden durch oxidativen Stress. Die Funktion der Selenoproteine ist bei Selenmangel gestört. So tritt die Keshan-Krankheit – eine Kardiomyopathie in Zusammenhang mit Coxsackie-Virusinfektionen – gehäuft auf, wenn es am Spurenelement Selen in der Nahrung mangelt;[3] auch die Kaschin-Beck-Krankheit kommt als Mangelsyndrom in Gegenden mit selenarmen Böden vor. Die Annahme jedoch, dass eine Nahrungsergänzung mit Selen generell Krebs vorbeuge, bestätigte die (SELECT-)Studie nicht.[4]

Biosynthetisch entsteht L-Selenocystein durch Selenylierung eines L-Serins, das an eine spezifische tRNA gebunden vorliegt:
Der Biosyntheseweg unterscheidet sich also deutlich von anderen Aminosäuren, welche zunächst als freie Aminosäuren gebildet und erst danach an eine tRNA gebunden werden.
Die tRNASec hat das Anticodon UCA und dieses Triplett, gegenläufig 3′-ACU-5′ notiert, kann mit dem Basentriplett des Codons UGA der mRNA paaren. Normalerweise bewirkt UGA als Stopcodon die Termination der Translation. Bilden jedoch besondere Sequenzen der mRNA eine Haarnadelstruktur aus, so wird es möglich, die beladene Sec-tRNASec mit dem Codon UGA zu paaren. Damit wird das Stopsignal ignoriert und Selenocystein an dieser Stelle in das Protein eingebaut. Dieser Vorgang wird auch als Recodierung bezeichnet.
Bei Bakterien findet sich eine solche Secis (selenocysteine insertion sequence) genannte Sequenz der mRNA in unmittelbarer Nachbarschaft zum Codon UGA und nur dieses benachbarte wird dann recodiert. Die Secis-Sequenz wird durch einen spezifischen GTP-abhängigen Translationsfaktor, den Elongationsfaktor SelB, erkannt, welcher zugleich die Sec-tRNASec bindet. Nach dem Einbau des Selenocysteins wird auch die Secis-Sequenz vom Ribosom abgelesen und übersetzt in entsprechende Aminosäuren des Proteins.

Bei Eukaryoten und Archaeen ist eine Secis-Sequenz hingegen am 3'-Ende der mRNA angebracht, wird nicht vom Ribosom abgelesen, und erlaubt es, alle Codons UGA dieser mRNA zu recodieren.[5] So enthält beispielsweise das menschliche Selenoprotein P an zehn Positionen Selenocysteine.[6]
Der Einbau von L-Selenocystein während der Proteinbiosynthese bei Eukaryoten bedarf weiterer Faktoren (siehe Abbildung):
UGA am Ribosom abgelesen und mit dem Anticodon der bereit gehaltenen Sec-tRNASec gepaart, so wird an dieser Position nun Selenocystein eingebaut.UAA oder UAG, beendet werden (in der Abbildung als Stop gekennzeichnet).Die Verhältnisse bei der Selenoproteinsynthese der Archaea sind noch nicht aufgeklärt.
Seamless Wikipedia browsing. On steroids.
Every time you click a link to Wikipedia, Wiktionary or Wikiquote in your browser's search results, it will show the modern Wikiwand interface.
Wikiwand extension is a five stars, simple, with minimum permission required to keep your browsing private, safe and transparent.