Loading AI tools
Da Wikipedia, l'enciclopedia libera
In genetica umana, gli aplogruppi del cromosoma Y sono raggruppamenti di combinazioni di marcatori (aplotipi) definiti dalle differenze nella regione non-ricombinante del DNA del cromosoma Y (chiamato NRY da Non-Recombining Y-chromosome). Queste differenze fanno riferimento a polimorfismi biallelici (SNPs, Single Nucleotide Polymorphisms).
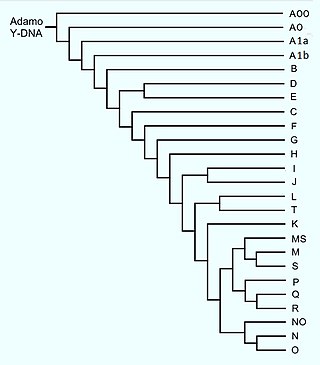
IL YCC Y Chromosome Consortium (archiviato dall'url originale il 16 gennaio 2017). ha stabilito un sistema per definire gli aplogruppi del cromosoma Y basato sulle lettere da A a T, con ulteriori divisioni usando numeri e lettere in pedice.
Il cromosoma Y ancestrale (scherzosamente definito dagli studiosi "Adamo") è quello appartenuto ad un maschio teorico che rappresenta il più recente progenitore comune (MRCA Most Recent Common Ancestor) di tutti i maschi attuali lungo la linea patrilineare, visto che il cromosoma Y è unicamente trasmesso dal padre ai figli maschi.
La stima di quando questo individuo teorico sia vissuto varia a seconda degli studi in un intervallo tra 200.000 e 300.000 anni fa.
Y, il cosiddetto "'Adamo ancestrale'"
Gli umani moderni, secondo studi del cromosoma Y, sono originari dell'Africa subsahariana e hanno poi colonizzato l'Eurasia (circa 70.000 anni fa)[27] seguendo la costa meridionale dell'Asia.[28] I gruppi che partirono dall'Africa si sarebbero successivamente dispersi secondo la seguente mappa:

Lo studio paleontologico sull'uomo di Neanderthal ha rivelato che l'aplotipo cromosomico Y del Neanderthal sarebbe estinto e la divergenza tra i Neanderthal e gli umani moderni si sarebbe verificata circa 590.000 anni fa.[29] La divergenza con l'Homo di Denisova, invece, sarebbe avvenuta circa 700.000 anni fa.[30]
L'analisi degli aplogruppi mitocondriali umani ha dato risultati molto simili; il consenso scientifico attuale è che le specie umane analizzate presentino le seguenti relazioni:[31]
|
I principali aplogruppi del cromosoma Y comprendono:
L'antenato comune di tutti i lignaggi è l'Adamo cromosomico con 275 000 anni.[32] I lignaggi del cromosoma Y più antichi sono il paragruppo A e il aplogruppo B, e si trovano particolarmente nell'Africa Sub-Sahariana o in popolazioni con la stessa origine come, per esempio, gli Afroamericani portati oltreoceano con la tratta degli schiavi. Le frequenze più importanti del gruppo parafiletico A si trovano tra i Boscimani, i Khung e i Sudanesi.[33] Le frequenze più elevate di B tra i Pigmei Biaka e Mbuti. Come si evince dall'albero filogenetico degli aplogruppi del cromosoma Y, tutta la diversità moderna si è generata in Africa, per cui le popolazioni contemporanee sono discendenti degli Africani che restarono in Africa o di quelle popolazioni che emigrarono fuori dall'Africa per popolare il resto dei continenti.

L'aplogruppo A è ancestrale e parafiletico. La sua relazione con B va secondo il seguente albero:
| Adamo−Y |
| ||||||||||||||||||||||||||||||||||||
Le mutazioni M168 e M294 (CT), assenti in A e B, definiscono tutti gli aplogruppi da C a T. Queste mutazioni precedettero la migrazione fuori dall'Africa, essendo presenti sia in Africa che al di fuori. Le mutazioni che caratterizzano DE (M1/YAP, M145) si verificarono in Africa più di 76 000 anni fa.[34] L'aplogruppo E rimase originariamente in Africa e le sue sottocladi più frequenti sono E1b1a e E1b1b. E1b1a-M2 (precedentemente chiamato E3a) riscontra la sua più alta frequenza e maggiore diversità in Africa Sub-Sahariana occidentale (più dell'80%).[35] D'altro canto, il sub-clade E1b1b (M215), precedentemente E3b, è di origine africana, è comune nei parlanti di lingue afro-asiatiche, la sua più grande diversità si trova in Etiopia e si disperse per tutto il mediterraneo raggiungendo le frequenze più alte nel Corno d'Africa e nel Nord Africa, essendo in Somalia l'81%;[36] e la frequenza del 27% in Grecia. L'aplogruppo D si trova soltanto nell'Himalaya e in pochissime zone nel sud del Giappone, dove fu introdotto dai primi colonizzatori. Le mutazioni tipiche che definiscono gli aplogruppi citati nel testo:
L'aplogruppo C è definito da M130/RPS4Y e M216, ha origine asiatica ed ha circa 53.000 anni.[37] Tra le popolazioni autoctone, le frequenze più alte del ramo C1 (F3393) sono in alcune parti dell'Oceania, come si può vedere nella Polinesia centrale e in Australia, poiché C1 si è disperso attraverso l'Asia meridionale, dirigendosi principalmente verso il sud-est, che è legato alla prima colonizzazione del sud-est asiatico e del continente di Sahul.[38]
Il ramo C2 si diffonde nell'Asia settentrionale ed è particolarmente comune nei popoli di lingue altaiche e na dené.[39]
L'aplogruppo F (M89) ha avuto origine circa 66.000 anni fa,[40] probabilmente nel subcontinente indiano[41] poiché è lì che si trova la maggiore diversità, con F1 (P91) in Sri Lanka, F3 (M481) nell'India sudoccidentale[42] e F2/F4 (Y27277) in Estremo Oriente.
Gli aplogruppi che discendono dall'aplogruppo F rappresentano il 90% della popolazione mondiale, ma si distribuiscono quasi esclusivamente fuori dall'Africa sub-sahariana. IJ corrisponde probabilmente a una ondata migratoria dal Medio-Oriente o all'Asia occidentale a partire da 45 000 anni fa, che si è poi diffusa in Europa con l'uomo di Cro-Magnon. L'aplogruppo G, originatosi anch'esso in Medio-Oriente, o forse più a Est in Pakistan, intorno a 30 000 anni fa, secondo alcuni studi potrebbe essersi diffuso in Europa nel Neolitico, oppure, vista la sua forte discontinuità, aver raggiunto l'Europa già nel Paleolitico. L'aplogruppo H si originò forse in India 30-40 000 anni fa, dove persistette fino a ridiffondere in epoche storiche con i Gitani. Mutazioni che caratterizzano gli aplogruppi citati nella sezione:

| Aplogruppo F |
| ||||||||||||||||||||||||||||||
L'aplogruppo I (M170) rappresenta circa un quinto dei cromosomi Y europei. È quasi esclusivo dell'Europa pertanto si ritiene che si sia originato in quest'area. Il più antico I (I*) trovato è quello di un individuo noto come Krems WA3 (Bassa Austria), risalente a circa 31.000 anni fa.[43] Nello stesso sito sono stati trovati anche due gemelli, entrambi assegnati all'aplogruppo I*.[44] È probabile che sia stato confinato nel rifugio balcanico durante la glaciazione e che poi si sia ridiffuso verso nord con il ritiro dei ghiacciai. Nonostante sia relativamente frequente negli scandinavi, nei sardi e nelle popolazioni balcaniche, questi popoli presentano subcladi differenti dell'aplogruppo I. Questo suggerisce che ognuna delle popolazioni ancestrali è oggi dominata da un particolare subclade che ha marcato una indipendente espansione della popolazione lungo diversi percorsi migratori durante e immediatamente dopo la glaciazione.
Le principali sub-cladi dell'aplogruppo I sono:
I1 (M253, M307, P30, P40) (ex I1a) con le più alte frequenze in Scandinavia, Islanda, e Europa nord- orientale. Nelle Isole britanniche la mutazione I1-M253 è spesso usata come marcatore delle invasioni vichinghe o anglosassoni.
I2 (S31) (ex I1b) che include I2a1 (P37.2) ovvero la forma più comune nei Balcani e in Sardegna (dove rappresenta l'aplogruppo più cospicuo con una percentuale del 38% tra i maschi Sardi nella variante I2a1a1, M26) e I2a2 (P214) che raggiunge discrete frequenze lungo le coste nord-occidentali dell'Europa continentale con un picco in Germania. Dalla linea I2a2 è derivato I2a2a1 (M284) tipico delle Isole Britanniche.
L'aplogruppo K si è originato probabilmente nell'Asia meridionale[45] e da lì si è diffuso in tutto il mondo.
Da esso si sono generate due cladi principali: LT (L298), oggi diffuso in Medio Oriente ed in Asia meridionale, zone dove è di notevole frequenza; e K2 o MNOPS (M526), che si sarebbe stabilito inizialmente nel sud-est asiatico, poiché questa regione costituisce il suo centro di espansione.[46]
L'aplogruppo K è caratterizzato dai seguenti aplotipi e dalle seguenti mutazioni:
| Aplogruppo K (M9) |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||
L'aplogruppo M è prevalente nelle isole della Papua Nuova Guinea. Gli aplogruppi N e O comparvero 35-40 000 anni fa in Asia orientale.
L'aplogruppo N si è originato probabilmente in Mongolia e si è diffuso fino all'estremo Oriente e la Siberia come ad ovest, essendo il gruppo più comune tra i popoli uralici. L'aplogruppo O si trova in Estremo Oriente. L'aplogruppo P si trova soprattutto come sottotipi Q o R (vedi il seguito), raramente non differenziato; si è evoluto probabilmente nell'Asia centrale o nella regione di Altai. Anche l'aplogruppo Q si è probabilmente originato nell'Asia settentrionale, ha migrato verso est ed ha raggiunto l'America del nord attraverso lo stretto di Bering.
Tutti gli aplotipi afferenti all'aplogruppo R condividono le mutazioni M207 (UTY2), M306 (S1), S4, S8, S9 e possono essere suddivisi in tre principali linee evolutive: R1a, R1b e R2.
La R1a potrebbe essersi originata nelle vicinanze dell'Iran circa 25.000 anni fa.[47] È associato alla cultura kurgan, nota per la domesticazione del cavallo (circa 5 000 anni fa). Questa linea è attualmente presente in Asia centrale, in India e nelle popolazioni slave dell'Europa orientale.
La linea R1b è la più comune nelle popolazioni europee. Nell'Irlanda occidentale raggiunge una frequenza prossima al 100%. Si è originata prima della fine dell'ultima glaciazione, in Asia occidentale.[48]
Non vi è prova dell'esistenza di R1b in Europa prima del neolitico; il più antico campione di R1b europeo è stato rinvenuto in Spagna ad Els Trocs ed ha un'età di circa 7 000 anni[49], ma gli R1b attualmente presenti in Europa occidentale non discendono dalla sua clade (V88, attualmente quasi del tutto assimilata). Si suppone che gli R1b europei siano giunti con le espansioni indoeuropee dalla Russia meridionale, in quanto nella Cultura di Jamna sono stati rinvenuti vari campioni di R1b-L23 (principale clade di R1b diffusa in Europa).[49]
R2 è comune nel subcontinente indiano. Presente anche nel Vicino Oriente, Caucaso e Asia Centrale.
Seamless Wikipedia browsing. On steroids.
Every time you click a link to Wikipedia, Wiktionary or Wikiquote in your browser's search results, it will show the modern Wikiwand interface.
Wikiwand extension is a five stars, simple, with minimum permission required to keep your browsing private, safe and transparent.