ARNr 16S
páxina de homónimos de Wikimedia From Wikipedia, the free encyclopedia
Remove ads
O ARNr 16S, é dicir, ácido ribonucleico ribosómico 16S (en inglés 16S rRNA) é o compoñente da subunidade menor de 30S (S son as unidades svedberg) do ribosoma procariota, o cal se une á secuencia Shine-Dalgarno. Os xenes que o codifican denomínanse xene do ARNr 16S e utilízanse para reconstruír filoxenias, debido ás lentas taxas de evolución desta rexión xénica.[2] Carl Woese e George E. Fox foron os dous investigadores pioneiros no uso do ARNr 16S en filoxenética en 1977.[3]

Nunha soa bacteria poden existir múltiples secuencias do xene de ARNr 16S.[4]
Remove ads
Funcións
Ten varias funcións:
- Igual que o ARNr 23S, ten un papel estrutural, actuando como armazón, definindo as posicións das proteínas ribosómicas.
- O extremo 3' contén a anti-secuencia Shine-Dalgarno, que se une augas arriba ao codón de inicio AUG do ARNm. O extremo 3' do ARNr 16S únese ás proteínas S1 e S21, que están implicadas na iniciación da síntese de proteínas.
- Interacciona con ARNr 23S, axudando na unión das dúas subunidades ribosómicas (50S+30S)
- Estabiliza os emparellamentos correctos codón-anticodón no sitio A do ribosoma por medio da formación dun enlace de hidróxeno entre o átomo N1 dos residuos de adenina 1492 e 1493 e o grupo 2'OH do esqueleto do ARNm.
Remove ads
Estrutura
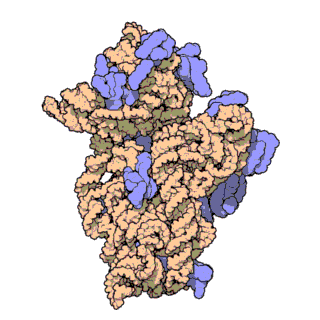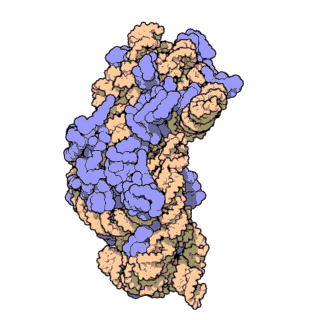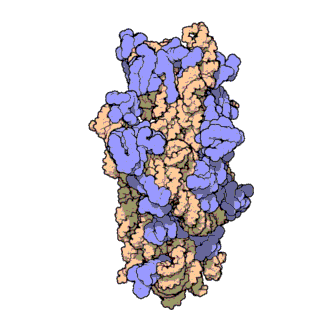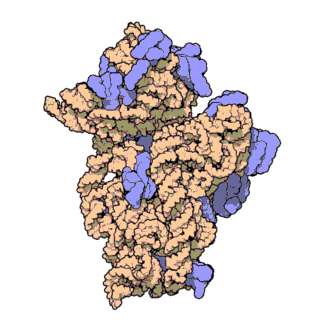
A súa estrutura pode dividirse en catro dominios, tal como se mostra na imaxe.

Cebadores universais
O xene do ARNr 16S utilízase para estudos filoxenéticos[5] xa que está altamente conservado entre diferentes especies de bacterias e arqueas.[6] Carl Woese foi o pioneiro neste uso do ARNr 16S.[2] Suxeriuse que o xene do ARNr 16S pode utilizarse como un reloxo molecular fiable porque as súas secuencias en distintas liñaxes bacterianas relacionadas distantemente teñen funcionalidades similares.[7] Algunhas arqueas (hiper)termófilas (por exemplo, as da orde Thermoproteales) conteñen intróns no xene do ARNr 16S que están localizados en rexións altamente conservadas e poden causar un impacto no annealing de cebadores "universais".[8] Os ARNr mitocondriais e cloroplásticos están tamén amplificados.
O par cebador ou primer máis común foi concibido por Weisburg et al.[5] e denomínase actualmente 27F e 1492R; porén, para algunhas aplicacións poden ser necesarios amplicóns máis curtos, como por exemplo o par cebador 27F-534R que cobre de V1 a V3 para a secuenciación 454 con química do titanio (as lecturas de 500 son ideais).[9] A miúdo utilízase o 8F en vez do 27F. Ambos os cebadores son case idénticos, pero o 27F ten un M en vez dun C. AGAGTTTGATCMTGGCTCAG comparado co 8F.[10]
Aplicacións en PCR e secuenciación
Ademais de sitios de unión de cebadores altamente conservados, as secuencias do xene do ARNr 16S conteñen rexións hipervariables que poden proporcionar secuencias sinatura específicas de especies útiles para a identiicación de bacterias.[15][16] Como resultado, a secuenciación do xene do ARNr 16S converteuse en algo común en microbioloxía médica como unha alternativa barata e rápida aos métodos fenotípicos de identificación bacteriana.[17] Aínda que a secuenciación do 16S se usou orixinalmente para identificar bacterias, viuse despois que servía para facer unha reclasificación das bacterias en especies completamente novas,[18] ou mesmo en xéneros.[5][19] Foron tamén usadas para describir novas especies que nunca se puideran cultivar con éxito.[20][21] Coa chegada a moitos laboratorios de técnicas de secuenciación de terceira xeración, é posible a identificación simultánea de miles de secuencias de ARNr 16S en cuestión de horas, o que permite facer estudos metaxenómicos, como por exemplo da flora intestinal.[22]
Rexións hipervariables
O xene do ARNr 16S bacteriano contén nove rexións hipervariables (V1-V9) que oscilan entre unha lonxitude de 30 a 100 pares de bases e que están implicadas na estutura secundaria da subunidade ribosómica menor.[23] O grao de conservación varía amplamente entre as rexións hipervaribles, e as rexións máis conservadas correlaciónanse coa taxonomía de maior nivel (grandes grupos) e as rexións menos conservadas coa de menor nivel, como xéneros e especies.[24] Aínda que as secuencias 16S completas permiten unha comparación de todas as rexións hipervariables, cando estas son de 1500 pares de bases de longo a súa análise pode ser prohibitivamente cara para estudos que tratan de identificar ou caracterizar diversas comunidades bacterianas.[24] Estes estudos utilizan habitualmente a plataforma Illumina, que produce lecturas de 50 a 12000 veces máis baratas que a pirosecuenciación 454 ou a secuenciación de Sanger, respectivamente.[25] Aínda que é máis barata e axeitada para cubrir máis profundmente unha comunidade,a secuenciación de Illumina só produce lecturas de 75 a 250 pares de bases de longo (ata 300 pares de bases con Illumina MiSeq), e non ten un protocolo establecido para a ensamblaxe fiable do xene completo en mostras da comunidade bacteriana.[26] Porén, as rexións completamente hipervariables poden ser ensambladas a partir dunha soa execución de Illumina, o que as fai dianas ideais para a plataforma.[26]
Aínda que as rexións hipervariables do 16S poden variar drasticamente entre bacterias, o xene do 16S en conxunto mantén unha maior homoxeneidade na lonxitude que o seu equivalente eucariota de 18S, o cal pode facer que os aliñamentos sexan máis doados.[27] Ademais, o xene do 16S contén secuencias altamente conservadas entre rexións hipervariables, o que permite o deseño de cebadores universais que poden producir fiablemente as mesmas seccións da secuencia do 16S en diferentes taxons.[28] Aínda que ningunha rexión hipedrvariable pode clasificar con exctitude todas as bacterias desde a categoría de dominio á de especie, algunhas poden predicir con fiabilidade niveis taxonómicos específicos.[24] Por esta razón, moitos estudos de comunidade seleccionan as rexións hipervariables semiconservadas como a V4, xa que pode proporcionar unha resolución a nivel de filo de maneira tan precisa coma o xene 16S completo.[24] Aínda que as rexións menos conservadas teñen dificultade para clasificar novas especies cando o nivel taxonómico superior se descoñece, utilízanse a miúdo para detectar a presenza de patóxenos específicos. Nun estudo feito por Chakravorty et al. en 2007, caracterizáronse as rexións V1-V8 de varios patóxenos para determinar que rexións hipervariables sería máis útil incluír para probas específicas de especie ou de espectro máis amplo.[29] Entre outros descubrimentos, estes investigadores atoparon que a rexión V3 era mellor para identificar o xénero de todos os patóxenos probados e que a V6 era a máis axeitada para diferenciar especies entre todos os patóxenos probados das listas da CDC estadounidense, incluíndo o ántrax.[29]
Aínda que a análise de rexións hipervariables 16S é unha poderosa ferramenta para os estudos de taxonomía bacteriana, ten dificultades á hora de diferenciar entre especies moi estreitmente emparentadas.[28] Nas familias Enterobacteriaceae, Clostridiaceae e Peptostreptococcaceae, as especies poden compartir ata o 99% en similitude de secuencia no xene 16S completo.[30] Como resultado, as secuencias V4 poden diferir en só uns poucos nucleótidos, o que fai que as bases de datos de referencia non poidan clasificar con fiabilidade estas bacterias nos niveis taxonómicos inferiores.[30] Limitando a análise do 16S a rexións hipervariables seleccionadas, estes estudos poden fracasar ao non observr diferenzas en taxóns estreitamente relacionados e agrupalos nunha soa unidade taxonómica, subestimando a diversidade total da mostra.[28] Ademais, os xenomas bacterianos poden conter múltiples xenes de ARNr 16S, e as rexións V1, V2 e V6 son as que conteñen a maior diversidade intraespecífica.[6] Aínda que non é o método máis preciso para clasificar as especies bacterianas, a análise de rexións hipervariables segue sendo unha das ferramentas máis útiles de que se dispón para estudos de comunidades bacterianas.[30]
Remove ads
Bases de datos de ARNr 16S
O xene do ARNr 16S utilízase como un estándar na clasificación e identificación de microbios, porque está presente na maioría dos microbios e presenta os cambios adecuados. Disponse de cepas tipo de secuencias do xene do ARNr 16S da maioría das bacterias e arqueas en bases de datos públicas como as do NCBI. Porén, con frecuencia a calidade das secuencias que se encontran nesas bases de datos non está validada. Por tanto, utilízanse moito bases de datos secundarias que recollen só secuencias de ARNr 16S. As bases de datos máis usadas son as seguintes:
EzBioCloud
A base de datos EzBioCloud, antes chamada EzTaxon, consta dun sistema taxonómico xerárquico que contén 62988 especies/filotipos de bacterias e arqueas, que inclúe 15290 nomes publicados validamente ata setembro de 2018. Baseándose nas relacións filoxenéticas como as de máxima probabilidade e OrthoANI, todas as especies/subespecies están representadas por polo menos unha secuencia do xene de ARNr 16S. A base de datos EzBioCloud está revisada sistematicamente e posta ao día regularmente, o que tamén inclúe novas especies candidatas. Ademais, a páxina web ofrece ferramentas bioinformáticas como unha calculadora ANI, ContEst16S e 16S rRNA DB para as pipeline Mothur e QIIME.[31]
The Ribosomal Database Project
The Ribosomal Database Project (RDP) Arquivado 19 de agosto de 2020 en Wayback Machine. é unha base de datos revisados que ofrece datos de ribosomas xunto con programas relacionados e servizos. As ofertas inclúen aliñamentos ordenados filoxeneticamente de secuencias de ARNr, árbores filoxenéticas derivadas, diagramas da estrutura secundaria do ARNr e varios paquetes de software para manexar, analizar e mostrar os aliñamentos e árbores. Os datos están dispoñibles por ftp e correo electrónico. Tamén se proporcionan certos servizos analíticos por servidor de correo electrónco.[32]
SILVA
SILVA proporciona conxuntos de datos completos de calidade comprobada e postos ao día regularmente de secuencias aliñadas de ARNr das subunidades ribosómicas menor (16S/18S, SSU) e maior (23S/28S, LSU) dos tres dominios da vida, así como unha suite de ferramentas de investigación, deseño de cebadores e aliñamento para Bacteria, Archaea e Eukarya.[33]
GreenGenes
Greengenes é unha base de datos de referencia de 16S completa e de calidade controlada, baseada na taxonomía dunha filoxenia de novo, que proporciona conxuntos de unidades taxonómicas operacionais estándar. A páxina oficial deste sitio é http://greengenes.secondgenome.com Arquivado 22 de xullo de 2019 en Wayback Machine., e ten licenza Creative Commons BY-SA 3.0.[34][35]
Remove ads
Notas
Véxase tamén
Wikiwand - on
Seamless Wikipedia browsing. On steroids.
Remove ads